Del 6 al 10 de julio se llevó adelante el 23 Congreso de la Sociedad Internacional de SIDA – AIDS2020, completamente en modalidad virtual debido a las conocidas limitaciones producto de la pandemia por COVID-19. El congreso reunió a los principales actores de la lucha contra el SIDA.
En el marco de este importante congreso fueron presentados resultados de un estudio realizado en colaboración entre Cibic y profesionales del Hospital Cosme Argerich y del Hospital Francisco J. Muñiz.
El trabajo titulado “Reverse transcriptase and protease inhibitors mutational viral load in HIV infected pregnant women with transmitted drug resistance in Argentina” fue seleccionado por el comité científico del congreso como e-Poster y fue presentado por el Dr. Diego Cecchini del Hospital Argerich. Para visualizar el e-Poster haga clic aquí.
Los resultados obtenidos en una cohorte de mujeres embarazadas VIH positivas del área metropolitana de la ciudad de Buenos Aires indican que las mutaciones asociadas a inhibidores no nucleósidos de la transcriptasa inversa (INNRT) se presentaban en la población viral predominante con carga viral mutacional superior a 1000 copias/ml. Dado que estas mutaciones se han encontrado frecuentemente en las pacientes embarazadas VIH positivas, este hallazgo indicaría un elevado riesgo de transmisión perinatal.
La carga viral mutacional se calcula a partir de la carga viral en plasma y del porcentaje de cuasiespecies virales mutadas obtenido por secuenciación ultraprofunda, y permite conocer qué tan representada se encuentra una variante mutante en la población de cuasiespecies que infectan al paciente.
Cibic implementó la secuenciación ultraprofunda en 2017 para sus test de resistencia y desde entonces ha presentado diferentes estudios que demuestran una mayor sensibilidad de esta metodología en la detección de mutaciones de resistencia con respecto a las metodologías convencionales. La posibilidad de calcular la carga viral mutacional a partir del resultado del test de resistencia es otra ventaja que ofrece esta metodología.
Prestaciones disponibles en Cibic:
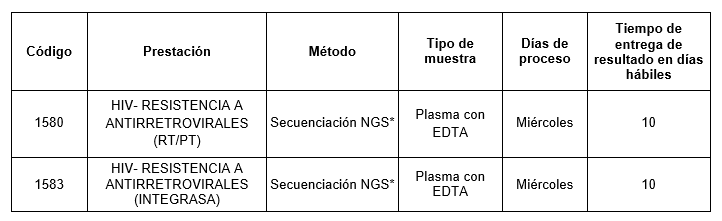
* Metodología: Secuenciación NGS.
A partir de la secuencia consenso obtenida por secuenciación NGS (profundidad 4000x) con filtro de 20% de sensibilidad y el algoritmo de la base de datos de la Universidad Stanford (HIVdb) se genera un informe de fenotipo virtual. En caso de requerirse se puede generar dicho informe aplicando filtros de sensibilidad
de 10%, 5% y 1%.
Referencias
e-Poster: “Reverse transcriptase and protease inhibitors mutational viral load in HIV infected pregnant women with transmitted drug resistance in Argentina”. Presentado en 23 Congreso de la Sociedad Internacional de SIDA – AIDS2020. Autores: D. Cecchini1, J. Sfalcin2, I. Zapiola3, A. Gomez2, S. Fernandez Giuliano3, L. Mammana3, A. Seravalle2, Fay F2, M.B. Bouzas3
1 Hospital Cosme Argerich, Infectious Diseases Unit, Buenos Aires, Argentina, 2 CIBIC Laboratorios, Rosario, Argentina, 3 Hospital Francisco J. Muñiz, Virology Unit, Buenos Aires, Argentina
Para mayor información o consultas:
Sección: Biología Molecular
Lic. Javier Sfalcin. Teléfono: 0341- 4722424. Interno: 241
Lic. Alan Gomez. Teléfono: 0341- 4722424. Interno: 243

